Por Phys.org:
Una momia boliviana reescribe el pasado de la escarlatina y sugiere que la bacteria mortal circulaba siglos antes de la colonización
por Eurac Research
editado por Stephanie Baum, revisado por Robert Egan
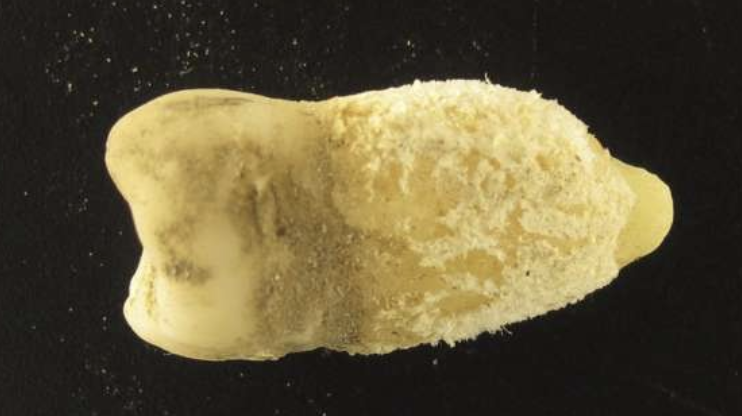
Este diente perteneció a un joven que vivió en el Altiplano boliviano hace alrededor de 700 años. El equipo de investigación detectó en él la bacteria de la escarlatina, Streptococcus pyogenes. Crédito: Guido Valverde
Investigadores han identificado material genético de la escarlatina al examinar un diente de un cráneo momificado de forma natural, conservado en el MUNARQ, el Museo Nacional de Arqueología en La Paz. Utilizando un método que reensambla genomas previamente desconocidos a partir de numerosos fragmentos cortos de ADN, reconstruyeron un genoma antiguo casi completo de Streptococcus pyogenes. El genoma reconstruido muestra claras similitudes con cepas modernas de esta bacteria ampliamente distribuida a nivel mundial, que puede causar una variedad de enfermedades, desde infecciones de garganta inofensivas hasta escarlatina y el síndrome de shock tóxico potencialmente mortal.
A pesar de la gran importancia médica de este patógeno —la escarlatina fue históricamente una de las principales causas de muerte entre los niños— se conoce poco sobre su historia evolutiva. Este hallazgo demuestra ahora que la bacteria ya circulaba entre poblaciones indígenas en Sudamérica antes de la colonización europea: el joven del cual proviene el diente vivió entre los años 1283 y 1383 d.C. El estudio resultante fue publicado en la revista Nature Communications.
“No estábamos buscando específicamente este patógeno”, enfatiza Frank Maixner, director del Instituto de Estudios de Momias de Eurac Research. “Al realizar análisis genéticos de momias, abordamos el trabajo con mente abierta, analizando no solo el material genético humano, sino también el ADN de los numerosos microorganismos presentes en los restos humanos”.
Entre los rastros de ADN bacteriano encontrados en el diente, Streptococcus pyogenes era frecuente. Debido a que el patógeno sigue siendo médicamente relevante hoy —con brotes de escarlatina en aumento en todo el mundo— el equipo analizó este material genético con mayor detalle.
Para reconstruir el genoma de varios siglos de antigüedad, los investigadores utilizaron el ensamblaje de novo, un método consolidado en la investigación genómica moderna que el Instituto de Estudios de Momias ha perfeccionado específicamente para ADN antiguo altamente fragmentado. Este método permite reconstruir un genoma a partir de muchos fragmentos de ADN sin utilizar un genoma de referencia como plantilla.
“Se puede pensar como armar un rompecabezas sin conocer la imagen de la caja”, explica el microbiólogo Mohamed Sarhan de Eurac Research, quien comparte la autoría principal del artículo con el bioquímico boliviano Guido Valverde.
“Este método tiene una gran ventaja para reconstruir genomas antiguos: no estamos influenciados por referencias modernas, trabajamos sin preconcepciones. Esto nos permite descubrir conocimientos completamente nuevos e identificar variantes genéticas que quizás ya no existen hoy, como cepas bacterianas extintas”.

Chullpas en el Altiplano boliviano. Estas torres funerarias son restos de una civilización que precedió al Imperio inca. Crédito: Juan Gabriel Estellano
Para el campo de investigación, esta posibilidad representa “algo así como el comienzo de una nueva era”, añade Maixner.
Dada su antigüedad, el ADN de la bacteria estaba relativamente bien conservado, lo que los investigadores atribuyen a las condiciones secas y frías de las tierras altas bolivianas. Este clima único también facilitó la momificación natural del cráneo, atribuido al Período Intermedio Tardío (1100–1450 d.C.). Mediante datación por radiocarbono y análisis genéticos, se determinó que el cráneo pertenecía a un joven de ascendencia indígena. Es probable, como ocurre con la mayoría de las otras momias del museo, que el cráneo haya sido encontrado en una chullpa, una de las típicas torres funerarias del Altiplano boliviano.
“La excelente preservación del ADN nos permitió reconstruir un genoma casi completo, lo que proporcionó una gran cantidad de información y demostró, por ejemplo, que la bacteria ya era capaz de causar enfermedad: la cepa antigua portaba muchos —aunque no todos— de los genes patogénicos presentes en las cepas modernas de Streptococcus pyogenes”, explica Valverde.

El bioquímico boliviano Guido Valverde en un almacén del Museo Arqueológico Nacional (MUNARQ) en La Paz. En los estantes: la colección de cráneos del museo. Crédito: Juan Gabriel Estellano
Este patógeno antiguo resultó ser particularmente similar a las cepas modernas que causan principalmente infecciones de garganta.
Durante una búsqueda dirigida en otros conjuntos de datos públicos de ADN antiguo, los investigadores encontraron Streptococcus pyogenes en 35 muestras de personas que vivieron en Europa hace unos 4.000 años, así como una especie estrechamente relacionada de Streptococcus en restos de gorilas africanos de hace 200 años, lo que demuestra que el patógeno ya estaba presente en muestras antiguas, pero había sido pasado por alto durante años.
Los análisis genéticos de los investigadores también indican que los linajes evolutivos de la mayoría de las cepas modernas de Streptococcus pyogenes divergieron hace unos 5.000 años, durante una época en que los seres humanos se volvían cada vez más sedentarios y vivían en mayor proximidad. Esto pudo haber facilitado la propagación y diversificación del patógeno, que se transmite principalmente por gotas respiratorias y contacto directo.
By Phys.org:
Bolivian mummy rewrites scarlet fever’s past, suggesting killer bacterium circulated centuries before colonization
edited by Stephanie Baum, reviewed by Robert Egan
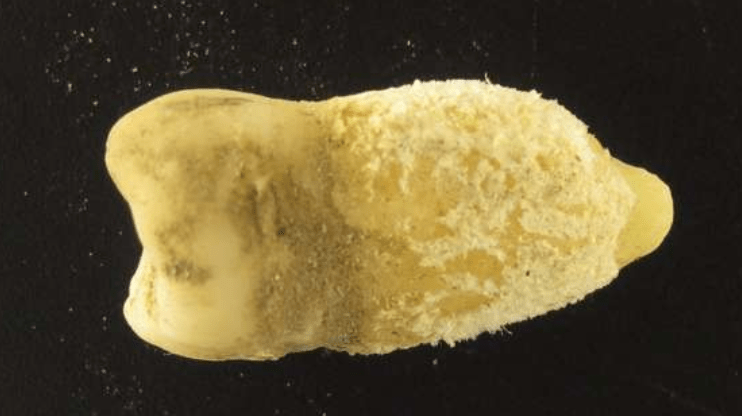
This tooth belonged to a young man who lived on the Bolivian Altiplano around 700 years ago. The research team detected the scarlet fever bacterium, Streptococcus pyogenes, inside it. Credit: Guido Valverde
Researchers have identified the genetic material of scarlet fever while examining a tooth from a naturally mummified skull housed at MUNARQ, the National Museum of Archaeology in La Paz. Using a method that reassembled previously unknown genomes from numerous short DNA fragments, they reconstructed a nearly complete, ancient genome of Streptococcus pyogenes. The reconstructed genome shows clear similarities to modern strains of the globally widespread bacterium, which can cause a variety of illnesses ranging from harmless throat infections to scarlet fever and life-threatening toxic shock syndrome.
Despite the pathogen’s great medical significance: scarlet fever was historically one of the leading causes of death among children, little is known about its evolutionary history. This finding now shows that the bacterium was already circulating among indigenous populations in South America before European colonization: the young man from whom the tooth originated lived between 1283 and 1383 AD. The resulting research paper is published in the journal Nature Communications.
“We weren’t looking for this pathogen specifically,” emphasizes Frank Maixner, director of the Eurac Research Institute for Mummy Studies. “When conducting genetic analyses of mummies, we approach the work with an open mind, analyzing not only human genetic material but also the DNA of the numerous microorganisms present in human remains.”
Among the bacterial DNA traces the researchers found in the tooth, Streptococcus pyogenes was common. Because the pathogen remains medically significant today—with scarlet fever outbreaks on the rise worldwide—the team analyzed this genetic material in greater detail.
To reconstruct the several-hundred-year-old genome, the researchers used de novo assembly, an established method of modern genome research that the Institute for Mummy Studies has further developed specifically for highly fragmented ancient DNA. It allows a genome to be reassembled from many DNA fragments without a reference genome as a template.
“You can think of it like putting together a puzzle without knowing the picture on the box,” explains Microbiologist Mohamed Sarhan of Eurac Research, who shares first authorship of the paper with Bolivian biochemist Guido Valverde.
“This method has a major advantage for reconstructing ancient genomes: we are not influenced by modern references—we work without preconceptions. This allows us to discover entirely new insights and also identify genetic variants that may no longer exist today, such as extinct bacterial strains.

Chullpas on the Bolivian Altiplano. These burial towers are the remains of a civilization that preceded the Inca Empire. Credit: Juan Gabriel Estellano
For the field of research, this possibility signifies “something like the beginning of a new era,” adds Maixner.
Given its age, the bacterium’s DNA was relatively well-preserved, which the researchers attribute to the dry and cold conditions in the Bolivian highlands. This unique climate also facilitated the natural mummification of the skull—attributed to the Late Intermediate Period (1100–1450 AD). Using radiocarbon dating and according to genetic analyses, it was found that the skull belonged to a young man of indigenous descent. It is likely, as is the case with most of the museum’s other mummies, that the skull was found in a chullpa, one of the typical burial towers of the Bolivian Altiplano.
“The DNA’s excellent preservation enabled us to reconstruct a nearly complete genome, yielding a wealth of information and demonstrating, for example, that the bacterium was already capable of causing disease: the ancient strain carried many—though not all—of the pathogenic genes found in modern Streptococcus pyogenes strains,” explains Valverde.

Bolivian biochemist Guido Valverde in a storage room at the National Archaeological Museum (MUNARQ) in La Paz. On the shelves: the museum’s collection of skulls. Credit: Juan Gabriel Estellano
This ancient pathogen was found to be particularly similar to modern strains that primarily cause throat infections.
During a targeted search of other publicly available datasets of ancient DNA, the researchers found Streptococcus pyogenes in 35 samples from people who lived in Europe about 4,000 years ago, as well as a closely related Streptococcus species in 200-year-old remains of gorillas from Africa, demonstrating that the pathogen was present already in ancient samples but had been overlooked for years.
The researchers’ genetic analyses also indicate that the evolutionary lineages of most modern Streptococcus pyogenes strains diverged around 5,000 years ago—during an era when humans were becoming increasingly sedentary and living in closer proximity. This may have facilitated the spread and diversification of the pathogen, which is primarily transmitted through droplet and contact transmission.
https://phys.org/news/2026-04-bolivian-mummy-rewrites-scarlet-fever.html
